RADNET: Genauigkeit auf radiologischer Ebene mithilfe von Deep Learning zur Erkennung von BLUTUNGEN bei CT-Scans
Autoren: Monika Grewal, Muktabh Mayank Srivastava, Pulkit Kumar, Srikrishna Varadarajan
Wir beschreiben einen Deep-Learning-Ansatz zur automatisierten Erkennung von Gehirnblutungen anhand von Computertomographie (CT) -Scans. Unser Modell emuliert das Verfahren, das Radiologen anwenden, um einen 3D-CT-Scan in der realen Welt zu analysieren. Ähnlich wie bei Radiologen durchsucht das Modell 2D-Querschnitte und achtet dabei besonders auf mögliche hämorrhagische Regionen. Darüber hinaus nutzt das Modell den 3D-Kontext aus benachbarten Schichten, um die Vorhersagen für jede Schicht zu verbessern, und aggregiert anschließend die Vorhersagen auf Schichtebene, um die Diagnose auf CT-Ebene zu stellen. Wir bezeichnen unseren vorgeschlagenen Ansatz als Recurrent Attention DenseNet (RadNet), da er die ursprüngliche DenseNet-Architektur verwendet und zusätzlich die Aufmerksamkeitskomponenten für Vorhersagen auf Schichtebene und eine rekurrente neuronale Netzwerkschicht zur Einbindung des 3D-Kontextes hinzufügt. Die reale Leistung von RadNet wurde mit unabhängigen Analysen verglichen, die von drei erfahrenen Radiologen für 77 Gehirn-CT durchgeführt wurden. RadNet weist auf CT-Ebene eine Genauigkeit von 81,82% zur Vorhersage von Blutungen auf, die mit der von Radiologen vergleichbar ist. Darüber hinaus erreicht RadNet eine höhere Erinnerungsrate als zwei der drei Radiologen, was bemerkenswert ist.
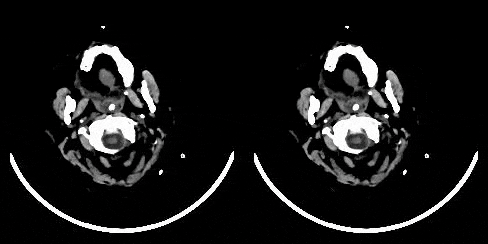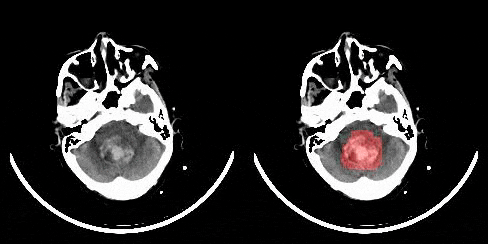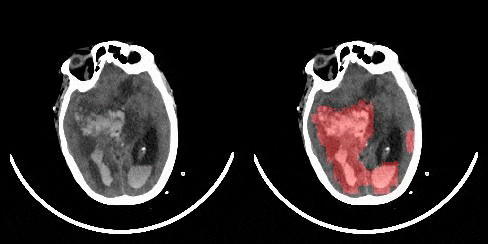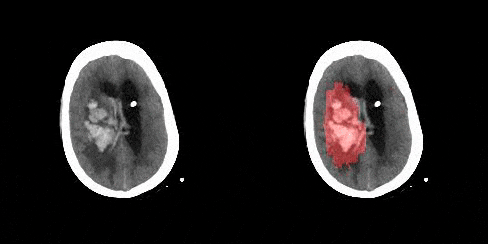
RadNet, unsere vorgeschlagene Architektur zur Erkennung von Gehirnblutungen, ahmt Radiologen nach, die versuchen, Blutungen im Gehirn zu erkennen, indem sie zwischen den CT-Schnitten nach unten gleiten oder nach oben rutschen, indem sie die Blutungserkennung als ein Sequenzmodellierungsproblem behandeln, bei dem die Elemente der Sequenzen 2D-CT-Schnitte sind. Ein Dense Convnet with Attention wird verwendet, um Dinge auf Slice-Ebene abzuleiten, und ein LSTM wird dann verwendet, um eine Sequenz von Slices zu klassifizieren. Im Vergleich zu Radiologen hatte RadNet eine vergleichbare Leistung wie Radiologen und einen besseren F1-Score als diese.
Anatomische Markierung von CT-Scan-Anomalien im Gehirn mithilfe von multikontextuellen Netzwerken zur engsten Nachbarschaftsbeziehung
Autoren: Srikrishna Varadarajan, Muktabh Mayank Srivastava, Monika Grewal, Pulkit Kumar
Diese Arbeit ist ein Bestreben, eine Deep-Learning-Methode für die automatische anatomische Markierung einer bestimmten Interessenregion (ROI) bei Computertomographie (CT) -Scans des Gehirns zu entwickeln. Wir kombinieren sowohl den lokalen als auch den globalen Kontext, um eine Darstellung des ROI zu erhalten. Anschließend verwenden wir Relation Networks (RNs), um die entsprechende Anatomie des ROI auf der Grundlage seines Beziehungswerts für jede Klasse vorherzusagen. Darüber hinaus schlagen wir eine neuartige Strategie vor, die den Ansatz der nächsten Nachbarn für das Training von RNs verwendet. Wir trainieren RNs darin, die Beziehung zwischen dem Ziel-ROI und der gemeinsamen Repräsentation der nächsten Nachbarn in jeder Klasse zu lernen, anstatt aller Datenpunkte in jeder Klasse. Die vorgeschlagene Strategie führt zu einem besseren Training der RNs und zu einer höheren Leistung im Vergleich zum Trainings-Basis-RN-Netzwerk.
Was wir hier vorschlagen, ist ein Meta-Learning-Algorithmus in dem Sinne, dass er klassenunabhängig ist und für jede neue Anatomie generalisiert werden kann, indem eine kleine Menge von Beispielen hinzugefügt wird (ein paar hundert Abschnitte). Der vorgeschlagene Algorithmus kann mit minimalem Aufwand effektiv auf eine beliebige Anzahl von Anatomien skaliert werden.
.png)
%20(1).png)
.jpg)